COVID-19 to choroba zakaźna wywoływana przez koronawirusa typu 2 zespołu ciężkiej ostrej niewydolności oddechowej. Kiedy osoba jest zarażona, najczęstsze objawy to gorączka, kaszel i duszność.
 Próbki użyte do badania można pobrać za pomocą wymazów z jamy nosowo-gardłowej lub ustno-gardłowej.
Próbki użyte do badania można pobrać za pomocą wymazów z jamy nosowo-gardłowej lub ustno-gardłowej.
Standardową metodą wykrywania koronawirusa jest reakcja łańcuchowa polimerazy, PCR.Jest to metoda szeroko stosowana w biologii molekularnej.Potrafi szybko skopiować miliony do miliardów określonych fragmentów DNA.
 Nowy koronawirus zawiera bardzo długi jednoniciowy genom RNA.Aby wykryć te wirusy metodą PCR, cząsteczki RNA muszą zostać przekształcone w ich komplementarne sekwencje DNA za pomocą odwrotnej transkryptazy, a następnie nowo zsyntetyzowany DNA może zostać zamplifikowany za pomocą standardowych procedur PCR, powszechnie znanych jako RT-PCR.
Nowy koronawirus zawiera bardzo długi jednoniciowy genom RNA.Aby wykryć te wirusy metodą PCR, cząsteczki RNA muszą zostać przekształcone w ich komplementarne sekwencje DNA za pomocą odwrotnej transkryptazy, a następnie nowo zsyntetyzowany DNA może zostać zamplifikowany za pomocą standardowych procedur PCR, powszechnie znanych jako RT-PCR.
Proces RT-PCR
Ekstrakcja RNA
Aby wykonać tę metodę, wirusowe RNA powinno zasadniczo zostać wyekstrahowane.Do wygodnej, szybkiej i skutecznej separacji można stosować różnorodne zestawy do oczyszczania RNA.
Aby wyekstrahować wirusowe RNA za pomocą dostępnego w handlu zestawu, najpierw dodaj próbkę do probówki do mikrowirówki, a następnie wymieszaj ją z buforem do lizy.Bufor ten jest wysoce zdenaturowany i zwykle składa się z fenolu i izotiocyjanianu guanidyny.Ponadto w buforze do lizy zwykle obecne są inhibitory RNazy, aby zapewnić izolację nienaruszonego wirusowego RNA.
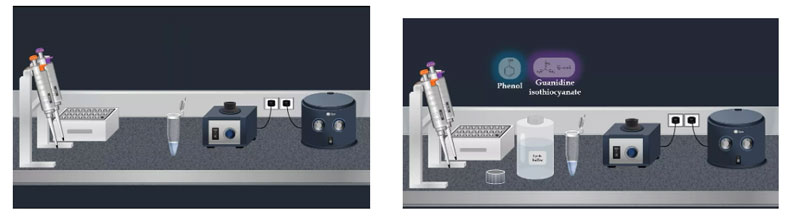 Po dodaniu buforu do lizy worteksować probówkę pulsacyjnie i inkubować w temperaturze pokojowej.Wirus jest następnie poddawany lizie w wysoce denaturujących warunkach zapewnionych przez bufor do lizy.
Po dodaniu buforu do lizy worteksować probówkę pulsacyjnie i inkubować w temperaturze pokojowej.Wirus jest następnie poddawany lizie w wysoce denaturujących warunkach zapewnionych przez bufor do lizy.
 Po lizie próbki do procedury oczyszczania stosuje się probówkę wirówkową.Próbkę umieszcza się w probówce wirówkowej, a następnie odwirowuje.
Po lizie próbki do procedury oczyszczania stosuje się probówkę wirówkową.Próbkę umieszcza się w probówce wirówkowej, a następnie odwirowuje.
 Ta procedura jest metodą ekstrakcji do fazy stałej, w której faza stacjonarna składa się z matrycy z żelu krzemionkowego.
Ta procedura jest metodą ekstrakcji do fazy stałej, w której faza stacjonarna składa się z matrycy z żelu krzemionkowego.
 W optymalnych warunkach soli i pH cząsteczki RNA wiążą się z membraną krzemionkową.
W optymalnych warunkach soli i pH cząsteczki RNA wiążą się z membraną krzemionkową.
 Jednocześnie usuwane są białka i inne zanieczyszczenia.
Jednocześnie usuwane są białka i inne zanieczyszczenia.
 Po odwirowaniu umieścić probówkę wirówkową w czystej probówce zbiorczej, odrzucić przesącz, a następnie dodać bufor do płukania.
Po odwirowaniu umieścić probówkę wirówkową w czystej probówce zbiorczej, odrzucić przesącz, a następnie dodać bufor do płukania.
 Ponownie umieść probówkę w wirówce, aby przepchnąć bufor płuczący przez membranę.To usunie wszystkie pozostałe zanieczyszczenia z membrany, pozostawiając tylko RNA związane z żelem krzemionkowym.
Ponownie umieść probówkę w wirówce, aby przepchnąć bufor płuczący przez membranę.To usunie wszystkie pozostałe zanieczyszczenia z membrany, pozostawiając tylko RNA związane z żelem krzemionkowym.
 Po przemyciu próbki umieść probówkę w czystej probówce mikrowirówki i dodaj bufor do elucji.
Po przemyciu próbki umieść probówkę w czystej probówce mikrowirówki i dodaj bufor do elucji.
 Następnie jest wirowany w celu przepchnięcia buforu do elucji przez membranę.Bufor do elucji usuwa wirusowe RNA z kolumny wirówkowej i uzyskuje oczyszczone RNA wolne od białek, inhibitorów i innych zanieczyszczeń.
Następnie jest wirowany w celu przepchnięcia buforu do elucji przez membranę.Bufor do elucji usuwa wirusowe RNA z kolumny wirówkowej i uzyskuje oczyszczone RNA wolne od białek, inhibitorów i innych zanieczyszczeń.
Mieszany koncentrat
Po ekstrakcji wirusowego RNA kolejnym krokiem jest przygotowanie mieszaniny reakcyjnej do amplifikacji PCR.Na tym etapie stosuje się koncentrat.Ten stężony roztwór jest wstępnie wymieszanym stężonym roztworem składającym się z przedmieszki, odwrotnej transkryptazy, nukleotydów, startera przedniego, startera wstecznego, sondy TaqMan i polimerazy DNA.
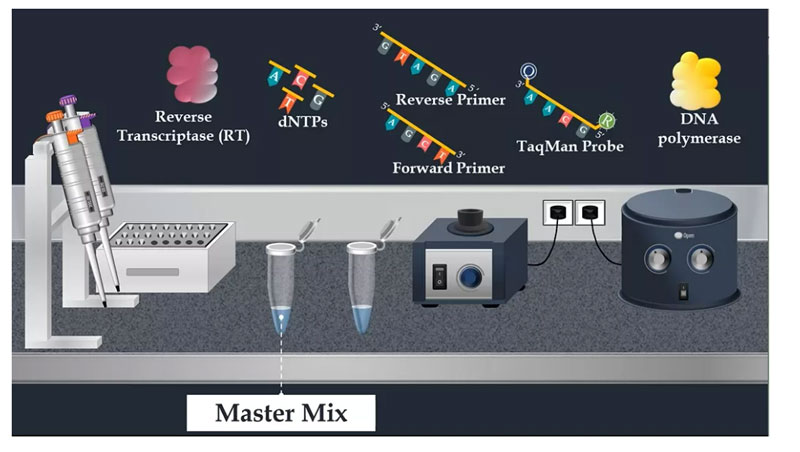 Na koniec, aby zakończyć tę mieszaninę reakcyjną, dodaje się matrycę RNA.Probówki miesza się przez pulsacyjne worteksowanie, a następnie mieszaninę reakcyjną umieszcza się na płytce do PCR.Płytka do PCR zawiera zazwyczaj 96 dołków i umożliwia jednoczesną analizę wielu próbek.
Na koniec, aby zakończyć tę mieszaninę reakcyjną, dodaje się matrycę RNA.Probówki miesza się przez pulsacyjne worteksowanie, a następnie mieszaninę reakcyjną umieszcza się na płytce do PCR.Płytka do PCR zawiera zazwyczaj 96 dołków i umożliwia jednoczesną analizę wielu próbek.
Amplifikacja PCR
Następnie umieść płytkę w urządzeniu do PCR, które zasadniczo jest termocyklerem.
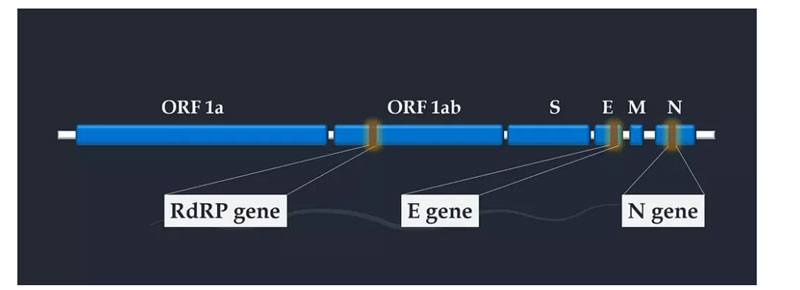
 Real-time RT-PCR służy do wykrywania nowego koronawirusa 2019 poprzez amplifikację sekwencji docelowej w genie RdrRP, genie E i genie N.Wybór genu docelowego zależy od sekwencji startera i sondy.
Real-time RT-PCR służy do wykrywania nowego koronawirusa 2019 poprzez amplifikację sekwencji docelowej w genie RdrRP, genie E i genie N.Wybór genu docelowego zależy od sekwencji startera i sondy.
 Pierwszym etapem RT-PCR jest odwrotna transkrypcja.Syntetyzowana jest pierwsza nić komplementarnego DNA, co jest inicjowane przez odwrotny starter PCR, który wiąże się z komplementarną częścią wirusowego genomu RNA.Następnie odwrotna transkryptaza dodaje nukleotydy DNA do końca 3' startera w celu syntezy DNA komplementarnego do wirusowego RNA.Temperatura i czas trwania tego etapu zależą od zastosowanych starterów, docelowego RNA i odwrotnej transkryptazy.
Pierwszym etapem RT-PCR jest odwrotna transkrypcja.Syntetyzowana jest pierwsza nić komplementarnego DNA, co jest inicjowane przez odwrotny starter PCR, który wiąże się z komplementarną częścią wirusowego genomu RNA.Następnie odwrotna transkryptaza dodaje nukleotydy DNA do końca 3' startera w celu syntezy DNA komplementarnego do wirusowego RNA.Temperatura i czas trwania tego etapu zależą od zastosowanych starterów, docelowego RNA i odwrotnej transkryptazy.
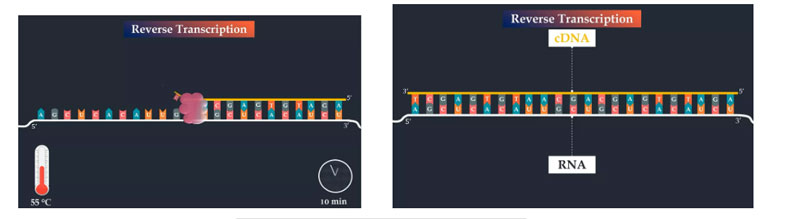 Następnie przeprowadzany jest wstępny etap denaturacji, w wyniku którego dochodzi do denaturacji hybrydy RNA-DNA.Ten krok jest niezbędny do aktywacji polimerazy DNA.W tym samym czasie odwrotna transkryptaza jest inaktywowana.
Następnie przeprowadzany jest wstępny etap denaturacji, w wyniku którego dochodzi do denaturacji hybrydy RNA-DNA.Ten krok jest niezbędny do aktywacji polimerazy DNA.W tym samym czasie odwrotna transkryptaza jest inaktywowana.
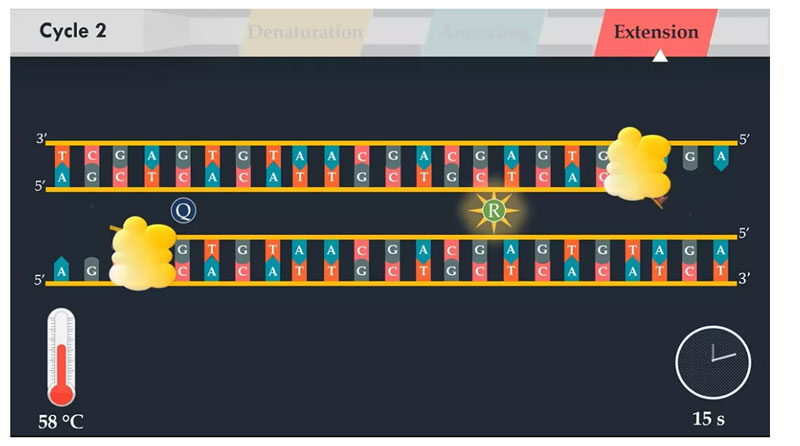
 PCR składa się z serii cykli termicznych.Każdy cykl składa się z etapów denaturacji, wyżarzania i wydłużania.
PCR składa się z serii cykli termicznych.Każdy cykl składa się z etapów denaturacji, wyżarzania i wydłużania.
 Etap denaturacji polega na podgrzaniu komory reakcyjnej do 95 stopni Celsjusza i użyciu jej do denaturacji matrycy dwuniciowego DNA.
Etap denaturacji polega na podgrzaniu komory reakcyjnej do 95 stopni Celsjusza i użyciu jej do denaturacji matrycy dwuniciowego DNA.
 W następnym etapie temperatura reakcji jest obniżana do 58 stopni Celsjusza, co umożliwia hybrydyzację startera przedniego z komplementarną częścią jednoniciowej matrycy DNA.Temperatura wyżarzania zależy bezpośrednio od długości i składu podkładu.
W następnym etapie temperatura reakcji jest obniżana do 58 stopni Celsjusza, co umożliwia hybrydyzację startera przedniego z komplementarną częścią jednoniciowej matrycy DNA.Temperatura wyżarzania zależy bezpośrednio od długości i składu podkładu.
 Na etapie wydłużania polimeraza DNA syntetyzuje nową nić DNA, która jest komplementarna do nici matrycy DNA.Poprzez dodanie wolnych jąder komplementarnych do matrycy w kierunku od 5' do 3' z mieszaniny reakcyjnej.Temperatura tego etapu zależy od użytej polimerazy DNA.
Na etapie wydłużania polimeraza DNA syntetyzuje nową nić DNA, która jest komplementarna do nici matrycy DNA.Poprzez dodanie wolnych jąder komplementarnych do matrycy w kierunku od 5' do 3' z mieszaniny reakcyjnej.Temperatura tego etapu zależy od użytej polimerazy DNA.
 Po pierwszym cyklu uzyskuje się docelowy dwuniciowy DNA.
Po pierwszym cyklu uzyskuje się docelowy dwuniciowy DNA.
 Następnie wejdź w drugi cykl.Dwuniciowy DNA jest denaturowany w celu wytworzenia dwóch jednoniciowych cząsteczek DNA.
Następnie wejdź w drugi cykl.Dwuniciowy DNA jest denaturowany w celu wytworzenia dwóch jednoniciowych cząsteczek DNA.
 W kolejnym etapie temperatura reakcji jest obniżana, startery są przyłączane do każdej matrycy jednoniciowego DNA, a sonda Taq-man jest przyłączana do komplementarnej części docelowego DNA.
W kolejnym etapie temperatura reakcji jest obniżana, startery są przyłączane do każdej matrycy jednoniciowego DNA, a sonda Taq-man jest przyłączana do komplementarnej części docelowego DNA.
 Sonda TaqMan składa się z fluoroforu kowalencyjnie połączonego z końcem 5' sondy oligonukleotydowej.Po wzbudzeniu przez źródło światła cyklera, fluorofor emituje fluorescencję.Ponadto sonda składa się z wygaszacza na końcu 3'.Bliskość genu reporterowego do wygaszacza uniemożliwia wykrycie fluorescencji.
Sonda TaqMan składa się z fluoroforu kowalencyjnie połączonego z końcem 5' sondy oligonukleotydowej.Po wzbudzeniu przez źródło światła cyklera, fluorofor emituje fluorescencję.Ponadto sonda składa się z wygaszacza na końcu 3'.Bliskość genu reporterowego do wygaszacza uniemożliwia wykrycie fluorescencji.
 Na etapie wydłużania polimeraza DNA syntetyzuje nową nić.Kiedy polimeraza dociera do sondy TaqMan, jej endogenna aktywność 5′nukleazy rozszczepia sondę, oddzielając barwnik od wygaszacza.
Na etapie wydłużania polimeraza DNA syntetyzuje nową nić.Kiedy polimeraza dociera do sondy TaqMan, jej endogenna aktywność 5′nukleazy rozszczepia sondę, oddzielając barwnik od wygaszacza.
 Z każdym cyklem PCR uwalnianych jest więcej cząsteczek barwnika, co powoduje wzrost intensywności fluorescencji proporcjonalny do liczby zsyntetyzowanych amplikonów.
Z każdym cyklem PCR uwalnianych jest więcej cząsteczek barwnika, co powoduje wzrost intensywności fluorescencji proporcjonalny do liczby zsyntetyzowanych amplikonów.
 Metoda ta pozwala na oszacowanie liczby danej sekwencji obecnej w próbce.Liczba dwuniciowych fragmentów DNA podwaja się w każdym cyklu.Dlatego PCR można wykorzystać do analizy bardzo małych próbek.
Metoda ta pozwala na oszacowanie liczby danej sekwencji obecnej w próbce.Liczba dwuniciowych fragmentów DNA podwaja się w każdym cyklu.Dlatego PCR można wykorzystać do analizy bardzo małych próbek.
 Do pomiaru sygnału fluorescencyjnego, halogenowej lampy wolframowej, filtra wzbudzenia, odbłyśnika, soczewki, filtra emisji i urządzenia ze sprzężeniem ładunkowym należy użyć kamery CCD.
Do pomiaru sygnału fluorescencyjnego, halogenowej lampy wolframowej, filtra wzbudzenia, odbłyśnika, soczewki, filtra emisji i urządzenia ze sprzężeniem ładunkowym należy użyć kamery CCD.
KROK 4 Wykryj
Do pomiaru sygnału fluorescencyjnego, halogenowej lampy wolframowej, filtra wzbudzenia, odbłyśnika, soczewki, filtra emisji i urządzenia ze sprzężeniem ładunkowym należy użyć kamery CCD.
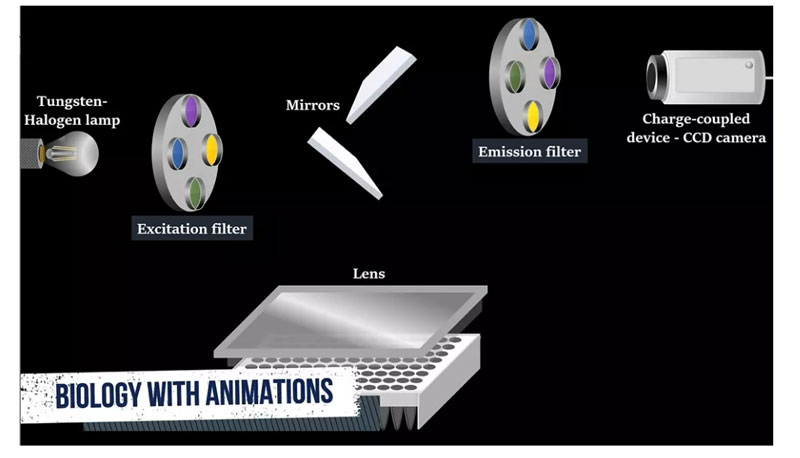 Przefiltrowane światło z lampy odbija się od reflektora, przechodzi przez soczewkę kondensora i skupia się na środku każdego otworu.Następnie fluorescencja emitowana z otworu odbija się od lustra, przechodzi przez filtr emisyjny i jest wykrywana przez kamerę CCD.W każdym cyklu PCR samowzbudne światło fluoroforu może być wykryte przez CCD.
Przefiltrowane światło z lampy odbija się od reflektora, przechodzi przez soczewkę kondensora i skupia się na środku każdego otworu.Następnie fluorescencja emitowana z otworu odbija się od lustra, przechodzi przez filtr emisyjny i jest wykrywana przez kamerę CCD.W każdym cyklu PCR samowzbudne światło fluoroforu może być wykryte przez CCD.
 Przetwarza przechwycone światło na dane cyfrowe.Metoda ta nosi nazwę PCR w czasie rzeczywistym i umożliwia monitorowanie w czasie rzeczywistym postępu reakcji PCR.
Przetwarza przechwycone światło na dane cyfrowe.Metoda ta nosi nazwę PCR w czasie rzeczywistym i umożliwia monitorowanie w czasie rzeczywistym postępu reakcji PCR.
Czas postu: 19 lipca 2021 r













